Foram encontradas 110 questões.
Disciplina: Agronomia (Engenharia Agronômica)
Banca: CESPE / CEBRASPE
Orgão: EMBRAPA
Em relação à engenharia de bioprocessos e processos bioquímicos, julgue os itens a seguir.
A modelagem matemática dos bioprocessos é fundamental para prever o comportamento do sistema e melhorar as condições de operação, possibilitando uma utilização mais eficaz e sustentável dos recursos.
Provas
Disciplina: Agronomia (Engenharia Agronômica)
Banca: CESPE / CEBRASPE
Orgão: EMBRAPA
Considerando o desenvolvimento e a aplicação de bioinsumos na agricultura, julgue os próximos itens.
Os efeitos de inoculantes microbianos podem manifestar-se no solo, nas proximidades da interação dos microrganismos com seus hospedeiros e também em tecidos e órgãos distantes desses microrganismos. A resistência sistêmica induzida é um exemplo desse último efeito.
Provas
Disciplina: Agronomia (Engenharia Agronômica)
Banca: CESPE / CEBRASPE
Orgão: EMBRAPA
Considerando o desenvolvimento e a aplicação de bioinsumos na agricultura, julgue os próximos itens.
Os efeitos de biofertilizantes, biopesticidas e bioestimulantes microbianos são únicos e específicos de cada gênero, às vezes de cada espécie. Com isso, é necessária a aplicação de inoculantes monomicrobianos separados para a promoção de cada efeito desejado, como fixação de nitrogênio, solubilização de fosfato e produção de fitormônios.
Provas
Disciplina: Agronomia (Engenharia Agronômica)
Banca: CESPE / CEBRASPE
Orgão: EMBRAPA
Considerando o desenvolvimento e a aplicação de bioinsumos na agricultura, julgue os próximos itens.
Bactérias promotoras de crescimento vegetal utilizadas como inoculantes agem por mecanismos diretos, em que mantêm relação endofítica com seus hospedeiros, e indiretos, quando permanecem apenas no solo sem contato direto com os hospedeiros.
Provas
| Isolado/Linhagem fúngica | Estratégia empregada | Rendimento do bioinsumo secretado (mg/kg/h)(1) |
|---|---|---|
| Selvagem | Microbiologia: Isolamento em meio de cultura seletivo | 980 |
| Mutante 1 | Modificação genética por irradiação UV | 4.000 |
| Mutante 2 | Transgenia em linhagem auxotrófica(2) | 6.000 |
| Mutante 3 | Edição gênica por sistema CRISPR-Cas(3) | 2.000 |
| Mutante 1 + Selvagem | Microbiologia: Cocultivo | 6.500 |
(1) Miligrama de bioinsumo produzido em 1 h por kg de massa fúngica úmida.
(2) Gene heterólogo e gene marcador de seleção para via metabólica essencial.
(3) Deleção de sítio alostérico em enzima alvo de retroalimentação negativa.
Partindo das informações apresentadas na tabela acima e considerando os conhecimentos acerca do desenvolvimento e da aplicação de bioinsumos, julgue os itens que se seguem.
A caracterização, o entendimento e a replicação dos fenótipos do mutante 1 são dificultados por estarem associados a mudanças em diferentes loci, gerando múltiplas e novas condições regulatórias e metabólicas.
Provas
| Isolado/Linhagem fúngica | Estratégia empregada | Rendimento do bioinsumo secretado (mg/kg/h)(1) |
|---|---|---|
| Selvagem | Microbiologia: Isolamento em meio de cultura seletivo | 980 |
| Mutante 1 | Modificação genética por irradiação UV | 4.000 |
| Mutante 2 | Transgenia em linhagem auxotrófica(2) | 6.000 |
| Mutante 3 | Edição gênica por sistema CRISPR-Cas(3) | 2.000 |
| Mutante 1 + Selvagem | Microbiologia: Cocultivo | 6.500 |
(1) Miligrama de bioinsumo produzido em 1 h por kg de massa fúngica úmida.
(2) Gene heterólogo e gene marcador de seleção para via metabólica essencial.
(3) Deleção de sítio alostérico em enzima alvo de retroalimentação negativa.
Partindo das informações apresentadas na tabela acima e considerando os conhecimentos acerca do desenvolvimento e da aplicação de bioinsumos, julgue os itens que se seguem.
Além de maior produção do bioinsumo, a mutante 2 possui maior estabilidade gênica e menor reversão de transformantes que as demais mutantes quando cultivadas em larga escala em meios ricos.
Provas
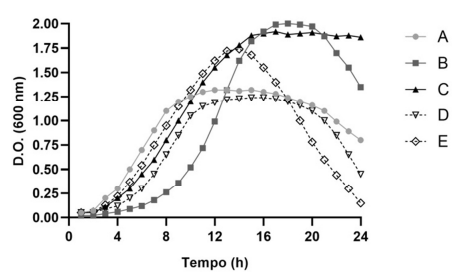
O gráfico acima apresenta os dados de crescimento bacteriano em sistema fechado (batelada) de diferentes isolados e linhagens. Os cinco cultivos foram realizados simultaneamente, em frascos separados e nas mesmas condições de espaço, volume, temperatura, agitação e meio de cultivo. A aferição do crescimento foi realizada a cada hora, no período total de 24 h, pela medição da turbidez do meio de cultivo líquido no comprimento de ondas de 600 nm. Os isolados selvagens A, B e C são da mesma espécie, mas foram obtidos de solos de diferentes regiões do Brasil. Após o sequenciamento e a comparação dos genomas dos 3 isolados, foi identificada uma deleção de 3 aminoácidos no sítio ativo da enzima X do isolado A e a inserção de um transposon na região 3` do gene codificante de uma bomba de H+ (prótons) da membrana citoplasmática do isolado B. O isolado C foi modificado por engenharia genética com a deleção dos mesmos 3 aminoácidos que são ausentes no sítio ativo da enzima X do isolado A, gerando a linhagem mutante D. O isolado C também foi modificado com a inserção do transposon observado no isolado B, no mesmo locus, gerando a linhagem mutante E.
Considerando as informações contidas no gráfico e no texto anteriormente apresentados, julgue os itens seguintes.
Nas condições de isolamento e cultivo em aerobiose, utilizadas para gerar os dados do gráfico, não seriam obtidas espécies fixadoras de nitrogênio como Rhizobium ssp. e Mesorhizobium spp., pois esses gêneros estão associados em simbiose anaeróbia com nódulos radiculares de leguminosas.
Provas

O gráfico acima apresenta os dados de crescimento bacteriano em sistema fechado (batelada) de diferentes isolados e linhagens. Os cinco cultivos foram realizados simultaneamente, em frascos separados e nas mesmas condições de espaço, volume, temperatura, agitação e meio de cultivo. A aferição do crescimento foi realizada a cada hora, no período total de 24 h, pela medição da turbidez do meio de cultivo líquido no comprimento de ondas de 600 nm. Os isolados selvagens A, B e C são da mesma espécie, mas foram obtidos de solos de diferentes regiões do Brasil. Após o sequenciamento e a comparação dos genomas dos 3 isolados, foi identificada uma deleção de 3 aminoácidos no sítio ativo da enzima X do isolado A e a inserção de um transposon na região 3` do gene codificante de uma bomba de H+ (prótons) da membrana citoplasmática do isolado B. O isolado C foi modificado por engenharia genética com a deleção dos mesmos 3 aminoácidos que são ausentes no sítio ativo da enzima X do isolado A, gerando a linhagem mutante D. O isolado C também foi modificado com a inserção do transposon observado no isolado B, no mesmo locus, gerando a linhagem mutante E.
Considerando as informações contidas no gráfico e no texto anteriormente apresentados, julgue os itens seguintes.
Entre os novos métodos de sequenciamento de ácidos nucleicos (NGS), o uso de nanoporos com leituras longas, devido à maior cobertura vertical e profundidade, seria o mais indicado para proceder à triagem metagenômica dos três diferentes solos e identificar as variações nos isolados A e B.
Provas

O gráfico acima apresenta os dados de crescimento bacteriano em sistema fechado (batelada) de diferentes isolados e linhagens. Os cinco cultivos foram realizados simultaneamente, em frascos separados e nas mesmas condições de espaço, volume, temperatura, agitação e meio de cultivo. A aferição do crescimento foi realizada a cada hora, no período total de 24 h, pela medição da turbidez do meio de cultivo líquido no comprimento de ondas de 600 nm. Os isolados selvagens A, B e C são da mesma espécie, mas foram obtidos de solos de diferentes regiões do Brasil. Após o sequenciamento e a comparação dos genomas dos 3 isolados, foi identificada uma deleção de 3 aminoácidos no sítio ativo da enzima X do isolado A e a inserção de um transposon na região 3` do gene codificante de uma bomba de H+ (prótons) da membrana citoplasmática do isolado B. O isolado C foi modificado por engenharia genética com a deleção dos mesmos 3 aminoácidos que são ausentes no sítio ativo da enzima X do isolado A, gerando a linhagem mutante D. O isolado C também foi modificado com a inserção do transposon observado no isolado B, no mesmo locus, gerando a linhagem mutante E.
Considerando as informações contidas no gráfico e no texto anteriormente apresentados, julgue os itens seguintes.
A identificação dos isolados A, B, C e suas variações genômicas poderia ser antecipada em uma bioprospecção metagenômica, mas as características fenotípicas observadas no gráfico são específicas de cada cultura pura em seu ambiente experimental.
Provas

O gráfico acima apresenta os dados de crescimento bacteriano em sistema fechado (batelada) de diferentes isolados e linhagens. Os cinco cultivos foram realizados simultaneamente, em frascos separados e nas mesmas condições de espaço, volume, temperatura, agitação e meio de cultivo. A aferição do crescimento foi realizada a cada hora, no período total de 24 h, pela medição da turbidez do meio de cultivo líquido no comprimento de ondas de 600 nm. Os isolados selvagens A, B e C são da mesma espécie, mas foram obtidos de solos de diferentes regiões do Brasil. Após o sequenciamento e a comparação dos genomas dos 3 isolados, foi identificada uma deleção de 3 aminoácidos no sítio ativo da enzima X do isolado A e a inserção de um transposon na região 3` do gene codificante de uma bomba de H+ (prótons) da membrana citoplasmática do isolado B. O isolado C foi modificado por engenharia genética com a deleção dos mesmos 3 aminoácidos que são ausentes no sítio ativo da enzima X do isolado A, gerando a linhagem mutante D. O isolado C também foi modificado com a inserção do transposon observado no isolado B, no mesmo locus, gerando a linhagem mutante E.
Considerando as informações contidas no gráfico e no texto anteriormente apresentados, julgue os itens seguintes.
O isolado C possui maior potencial de aproveitamento de metabólitos secundários devido à longa fase de crescimento exponencial, principal estágio de síntese dos metabólitos primários pelas peptídeo-sintetases não ribosomais (NRPS).
Provas
Caderno Container